标签:perimeter area 模型 campactness 贝叶斯 seed R2jags rjags
原文链接:https://www.cnblogs.com/tecdat/p/11121891.html
本文是通过对area,perimeter,campactness几个变量的贝叶斯建模,来查看他们对groovelength这个变量的影响.
并且对比rjagsR2jags和内置贝叶斯预测函数的结果。
读取数据
read data
seed=read.csv("seeds_dataset.csv")seed=seed[,1:7]
查看数据的结构str(seed)
'data.frame': 209 obs. of 7 variables: $ area : num 14.9 14.3 13.8 16.1 14.4 ... $ perimeter : num 14.6 14.1 13.9 15 14.2 ... $ campactness : num 0.881 0.905 0.895 0.903 0.895 ... $ length : num 5.55 5.29 5.32 5.66 5.39 ... $ width : num 3.33 3.34 3.38 3.56 3.31 ... $ asymmetry : num 1.02 2.7 2.26 1.35 2.46 ... $ groovelength: num 4.96 4.83 4.8 5.17 4.96 ...
建立回归模型
Do a linear model
lm(formula = groovelength ~ area + perimeter + campactness, data = seed) Residuals: Min 1Q Median 3Q Max -0.66375 -0.10094 0.00175 0.11081 0.45132 Coefficients: Estimate Std. Error t value Pr(>|t|) (Intercept) 19.46173 2.45031 7.943 1.29e-13 *** area 0.49724 0.08721 5.701 4.10e-08 *** perimeter -0.63162 0.18179 -3.474 0.000624 *** campactness -14.05218 1.34325 -10.461 < 2e-16 *** --- Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1 Residual standard error: 0.1608 on 205 degrees of freedom Multiple R-squared: 0.895, Adjusted R-squared: 0.8934 F-statistic: 582.4 on 3 and 205 DF, p-value: < 2.2e-16
从回归模型的结果来看,三的自变量对因变量都有显著的意义。其中,area有正向的意义。而其他两个变量是负向的影响。从r方的结果来看,达到了0.895,模型具有较好的解释度。
使用arm软件建立贝叶斯回归模型
Bayesian analysis With bayesglm
bayesglm(formula = groovelength ~ area + perimeter + campactness, data = seed) Deviance Residuals: Min 1Q Median 3Q Max -0.66331 -0.09974 -0.00002 0.11110 0.44841 Coefficients: Estimate Std. Error t value Pr(>|t|) (Intercept) 18.90538 2.41549 7.827 2.63e-13 *** area 0.47826 0.08604 5.559 8.40e-08 *** perimeter -0.59252 0.17937 -3.303 0.00113 ** campactness -13.74353 1.32463 -10.375 < 2e-16 *** --- Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1 (Dispersion parameter for gaussian family taken to be 0.02584982) Null deviance: 50.4491 on 208 degrees of freedom Residual deviance: 5.2992 on 205 degrees of freedom AIC: -164.91 Number of Fisher Scoring iterations: 6
从内置贝叶斯模型的结果来看,3个变量同样是非常显著,因此模型的结果和回归模型类似。然后我们使用BUGS/JAGS软件包来建立贝叶斯模型
使用 BUGS/JAGS软件包来建立贝叶斯模型library(R2jags)
library(coda)
建立贝叶斯模型
jags(model.file='bayes.bug',parameters=c("area","perimeter","campactness","int"),data =list('a' =seed$area, 'b' =seed$perimeter, 'c' =seed$campactness, 'N'=N, 'y'=groovelength),n.chains =4,inits=NULL)
查看模型结果:
module glm loaded
Compiling model graph Resolving undeclared variables Allocating nodes Graph information: Observed stochastic nodes: 209 Unobserved stochastic nodes: 5 Total graph size: 1608
Initializing model
library('R2jags')bb <-jags1$BUGSoutput extract the "BUGS output" componentmm <-as.mcmc.bugs(bb) convert it to an "mcmc" object that coda can handleplot(jags1) large-format graph

从上面的图中,我们可以看到哥哥自变量的中位数和置信区间。从置信区间来看,各个变量的取值和内置贝叶斯模型的结果类似。内置贝叶斯结果的值全部落入在了置信区间内。
然后绘制每次迭代中各个变量参数的轨迹图
trace + density plots, same as above prettier trace plot
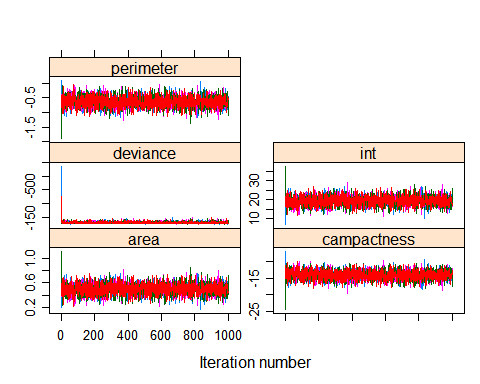
可以看到每个变量的参数都在一定区间内波动。同时可以看到误差在一定的迭代次数之后趋于收敛。
然后绘制每个变量参数的密度图
prettier density plot
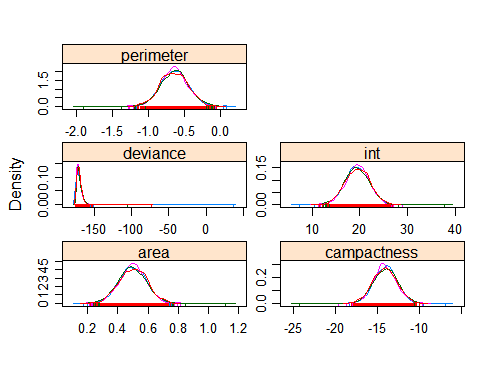
可以看到每个变量的参数,的密度分布近似于正态分布。同时我们可以看到分布的均值和内置贝叶斯模型,得到的结果类似。
然后绘制每个变量参数的置信区间
estimate + credible interval plot

从结果来看,可以看到各个变量参数的置信区间,campatness和int的置信区间较大,而其他两个变量的置信区间较小。
从上面的实验结果对比,我们可以看到,三个自变量对因变量均有重要的影响。area,perimeter,campactness几个变量他们对groovelength这个变量均有重要的影响.同时我们可以认为回归模型的结果和内置贝叶斯模型的结果相似。然后我们使用rjags&R2jags软件包来对数据进行贝叶斯型的建立,从结果来看,同样和之前得到的模型结果相差不大。并且我们通过模型的迭代,可以得到每个参数的置信区间。
标签:perimeter,area,模型,campactness,贝叶斯,seed,R2jags,rjags 来源: https://blog.csdn.net/qq_19600291/article/details/73648163
本站声明: 1. iCode9 技术分享网(下文简称本站)提供的所有内容,仅供技术学习、探讨和分享; 2. 关于本站的所有留言、评论、转载及引用,纯属内容发起人的个人观点,与本站观点和立场无关; 3. 关于本站的所有言论和文字,纯属内容发起人的个人观点,与本站观点和立场无关; 4. 本站文章均是网友提供,不完全保证技术分享内容的完整性、准确性、时效性、风险性和版权归属;如您发现该文章侵犯了您的权益,可联系我们第一时间进行删除; 5. 本站为非盈利性的个人网站,所有内容不会用来进行牟利,也不会利用任何形式的广告来间接获益,纯粹是为了广大技术爱好者提供技术内容和技术思想的分享性交流网站。

